v6.6 で追加された機能
pKa Model
ADME QSAR モジュールに含まれる StarDrop の新しい pKa モデルは、量子力学と機械学習を組み合わせて、一塩基酸及び二塩基酸化合物の酸解離定数を精度良く予測します。厳密に検証されたモデルは、 SAMPL6 テストセット( pKa 予測ベンチマーク用)などの複数の外部ベンチマークにおいて優れたパフォーマンスを発揮します。
詳細は、こちらのビデオ をご覧ください。
SeeSAR™
StarDrop6.6 では、StarDropの structure-based design 向け機能をより強力にする SeeSAR モジュール拡張スイートを提供します。
View
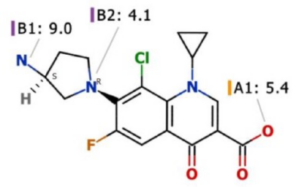
結合親和性を促進するキーとなる相互作用を特定する為のたんぱく質とリガンドを3Dで可視化します。X線結晶構造やご使用のドッキングソフトウェアでの予測結果の構造取り込みが可能です。
Affinity
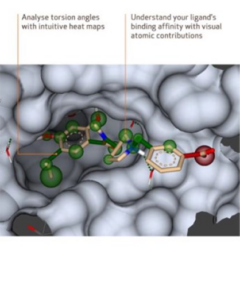
受賞歴のある HYDE スコアリングメソッドを使用し、リガンドの結合親和性を各原子の結合自由エネルギーへの寄与を可視化することにより分析したり、ねじれ角ヒートマップを表示してドッキングポーズを評価することが可能です。
Pose
FlexX docking を使用して、バーチャルスクリーニングのための複数ポーズの生成やインタラクティブな3Dデザインを行えます。
高速テンプレートドッキングにより、確立された結合モードを維持しながら、リアルタイムなフィードバックによる化合物編集を行うことが可能です。また、 SeeSAR Affinity モジュールと組み合わせることで、結合エネルギーに対する新しい最適化の影響を評価することが可能となります。
View および Affinity モジュールは、結晶構造または任意のドッキングソフトウェアの3Dポーズを取り込めます。
その他の拡張
- 大規模なデータセット検索時に特に有効となるカラム検索機能
- PowerPoint への出力ツールの強化、Mac 及び Keynote のサポート
- ChemDraw の mol フォーマットのコピー&ペーストのサポート
- その他多数
Optibrium Community
StarDrop の機能は、継続的に拡張および更新しているさまざまな無料アドオンで拡張する事が出来ます。 Optibrium Community Web サイトにログインし、無料でダウンロードする事が出来ます。 StarDrop 6.6 で引き続き機能させるには、アドオンの更新が必要な場合がありますのでご注意下さい。
最近追加された無料アドオンの拡張機能
REAL Space Search Tool
このツールを使用すると、対象のクエリ構造に類似する化合物を「Enamine REAL space」で検索できます。「Enamine REAL space」は現在、110億を超えるバーチャル化合物を収録しています。このツールは、 BioSolveIT の REAL Space Navigator と同じ様に FTrees テクノロジーを使用し膨大な REAL スペースをすばやく検索します。
- 化合物の局所的な化学空間の調査が可能
- 特性が改善された構造的に新しいリード化合物を見つけることや特許で保護されたスペースを避けることが可能
ICSYNTH light
このスクリプトを使用すると、「 ICSYNTH light 」にアクセスし、StarDropのインタラクティブデザイナーまたは Nova モジュールで設計された新しい分子の合成経路の評価が可能となります。「 ICSYNTH light 」は、トランスフォームベースのアプローチを採用しており新規若しくは未公開であってもターゲット分子の合成経路を生成します。このスクリプトは、可能な合成経路をWebブラウザーで表示します。
ChEMBL Search Tool
ChEMBL は、ドラッグライクな特性を持つ生理活性化合物を手作業で厳選した主要なデータベースです。化学、生理活性、ゲノムデータを纏め、ゲノム情報の効果的な新薬への展開を支援します。最近更新されたスクリプトを使用すると、 StarDrop から ChEMBL を直接検索し、事前定義したデータ形式で出力できる為、以下の業務で直ぐに利用可能となります。
- 化合物の潜在的なオフターゲットアクティビティの特定
- 化合物またはターゲット周辺の SAR の理解
- 新しい化合物の予測を行うための QSAR モデルの構築
v6.5 で追加された機能
データの可視化
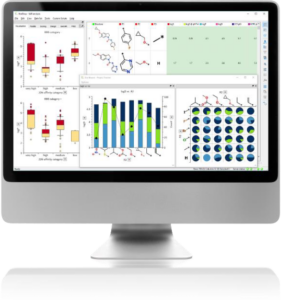
データ可視化機能が強化されました。グラフの種類およびフォーマットオプションの追加と共に、ユーザインターフェイスの合理化がなされました。わずか数回のクリックのみで、印刷品質のグラフを作成することが可能です。
新たに Dashboard 機能が追加されました。Dashboard 機能では複数のインタラクティブな図の統合、Dashboard 画面内での自由なレイアウト、Dashboard 画面の保存が可能です。チーム内での解析結果の共有促進を図るとともに、チームリーダーやマネージャーにおいては、ひと目でプロジェクトの進捗状況を確認することが可能となります。
データの可視化
データ可視化機能が強化されました。グラフの種類およびフォーマットオプションの追加と共に、ユーザインターフェイスの合理化がなされました。わずか数回のクリックのみで、印刷品質のグラフを作成することが可能です。
新たに Dashboard 機能が追加されました。Dashboard 機能では複数のインタラクティブな図の統合、Dashboard 画面内での自由なレイアウト、Dashboard 画面の保存が可能です。チーム内での解析結果の共有促進を図るとともに、チームリーダーやマネージャーにおいては、ひと目でプロジェクトの進捗状況を確認することが可能となります。

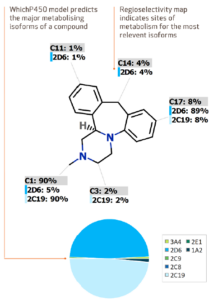
WhichP450™ モデル追加
新機能として、P450 モジュールに WhichP450 モデルが追加されました。WhichP450 では、ターゲット化合物が phase I 代謝において、どの Cytochrome P450 アイソフォームによって最も代謝されやすいかに関する情報を提供します。各アイソフォームによる代謝部位の位置選択制モデルとの統合により、P450代謝における主代謝物を予測することが可能となります。化合物がどのように代謝されるかを理解することは、その潜在的代謝物質の同定や分析、患者集団全体への投薬における Drug-Drug 相互作用または変化のリスクを低減させながらの化合物デザインを可能とします。
WhichP450 の詳細につきましては、Paper をご覧ください。
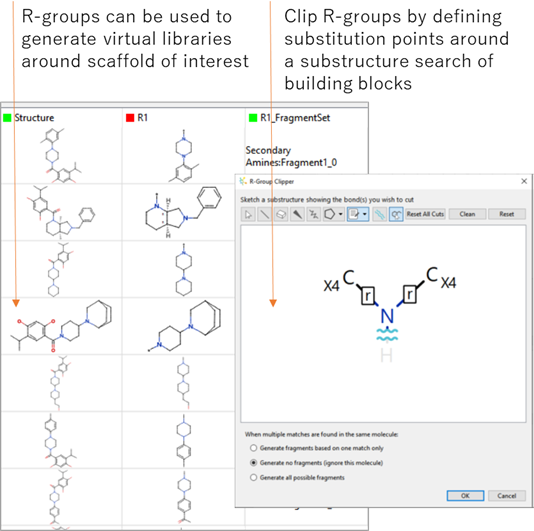
R-group clipping
StarDrop の新しい R-Group clipping 機能は、合成原料をそれらの関連置換基グループに、すばやく変換することを可能とします。Nova モジュールの利用により、即座にバーチャルライブラリを作成し、新しいデザイン仮説の探求を可能とします。最良の化合物合成に利用する原料発注支援のために、列挙された化合物と各原料の在庫状況や価格などの関連データはリンクされます。
フラグメントライブラリには、R-Group データおよび対応する合成原料の関連データを保存することが可能であり、簡単に同僚と情報共有することが可能です。各研究室や各ユーザが最も一般的に利用する置換基グループを用いたバーチャルライブラリを、迅速に作成することが可能となります。
Clipping 機能および R-Group 定義に基づいたバーチャルライブラリ作成手順は、開発元の R-group clipping of reagents for library enumeration をご覧ください。
その他の機能強化や変更点
- データセットや CardView に、定量的なデータと共に、イメージ図を埋め込むことが可能となりました。
- データセットから構造的に類似したものを探索する際、さらに柔軟性のある置換基探索が可能となりました。
- Refresh 機能が強化され、StarDrop project ファイルを開く際の自動データ更新、複数データソースからマージしたデータセットの更新が可能となりました。
- BIOSTER モジュールが更新されました。約 30,000 件の前例のある変換ルール(オリジナル文献参照情報あり)が含まれ、Nova モジュールにて利用可能です。
v6.4 で追加された機能
Docking および Alignment
StarDrop の新機能である Pose Generation Interface により、専門家のアドバイスに従った 3次元Docking & Alignment モデルと、データの可視化・2D SAR 解析・2D ADME 予測とのシームレスな連携が、洗練された統合環境にて実現可能となります。
このような環境により、3次元ベースでの複数相互作用評価を、リアルタイムで行っていただけます。また、実測値や各種 ADME 予測値を考慮しながらの Docking ポーズ結果調査が可能となり、重要な結合相互作用の理解を促進します。
Pose Generation Interface の利用により、計算化学者らは、自ら確証した 3次元モデルを、簡単に同僚へ提供することが可能となります。Pose Generation Interface は、以下に示す主要なドッキングシミュレーションソフトウェアとの互換性があります。

- FlexX™ – BioSolveIT
- Gold™ – Cambridge Crystallographic Data Centre
- MOE™ – Chemical Computing Group
- AutoDock Vina – The Scripps Research Institute
- POSIT™ – OpenEye Scientific
- 開発元の動画
Pose Generation Interface は、StarDrop6.4 の無償アドオンとして利用可能です。
Copy および Paste 機能の強化
Copy & Paste の機能強化により、選択した化合物のいかなる情報 (識別子や構造など) も StarDrop からダイレクトに Copy し、Excel / Word / PowerPoint へ Paste することが可能となりました。この機能強化により、研究結果のプレゼンや情報共有のためのサマリーテーブルを、簡単に作成できるようになります。
SeeSAR™ および BIOSTER™ モジュール
タンパク質-リガンド複合体の可視化ツールである SeeSAR モジュールが、さらに機能強化されました。SeeSAR アプリケーションのフルライセンスを所有している場合、StarDrop 内の構造情報やデータを、SeeSAR へとシームレスに転送できます。情報転送後、SeeSAR 画面内にて、結合サイト情報を踏まえた3 次元ベースでの構造編集や、BioSolvIT 社オリジナルの HYDE スコアリングおよび二面角解析などの追加計算が可能となります。SeeSAR タブの ![]() ボタンをクリックするだけで、SeeSAR アプリケーションが起動します。また、SeeSAR 画面の
ボタンをクリックするだけで、SeeSAR アプリケーションが起動します。また、SeeSAR 画面の ![]() ボタンをクリックするだけで、SeeSAR アプリケーション内での計算結果を StarDrop に転送することが可能です。
ボタンをクリックするだけで、SeeSAR アプリケーション内での計算結果を StarDrop に転送することが可能です。
BIOSTER モジュールもアップデートされ、先例のある変換ライブラリが 28,000 件を超えました。BIOSTER モジュールは Nova モジュールと組合わせて利用し、オリジナル文献の参照情報を含みます。

その他の機能強化や変更点
- Enhanced Stereochemistry をフルサポート (読込み・書き出し・編集) しました。
- パフォーマンスやメモリ利用を、大きく改良しました。この改良により、大規模データセットの利用が、容易になりました。
- StarDrop の Function Editor に、新たな関数が追加されました。関数追加により、StarDrop 画面内にて直接、テキスト操作やデータ収集、および、条件付きデータによる適切な計算などが可能となりました。toolbar の
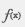 ボタンをクリックし、新しい関数をご確認ください。
ボタンをクリックし、新しい関数をご確認ください。
v6.3 で追加された機能
SeeSAR Module
新しい SeeSAR モジュールは、ターゲットタンパク質に対する化合物の結合状態を 3次元で可視化して理解するために、最先端で科学的に正確なアプローチを提供します。
StarDrop における SeeSAR モジュールは、X線結晶構造解析による結果やドッキングシミュレーションソフトにより予測された 3次元構造をシームレスに利用できます。SeeSAR による 3次元の情報と従来の StarDrop における 2次元構造に基づくケモインフォマティクス解析や描画を直感的に結びつけることにより、構造活性相関 (SAR) に新しい知見をもたらし、より最適な化合物設計を支援します。さらに、3次元モデルの結果が全てのディシジョンメーカーで共有可能となることにより、計算化学者と合成化学者の共同研究を促進します。
SeeSAR モジュールは StarDrop のオプションモジュールとして提供されます。
SeeSAR の Worked Example とデモンストレーションは こちら をご覧ください。

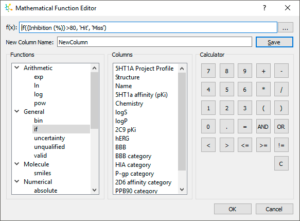
部分構造検索ツール
部分構造が一致する化合物を検索するための機能が飛躍的に強化、改善されました。以下のように、リンカーに対して長さや環構造を含むかを指定できるといった、柔軟な条件で検索ができます。
「原子」に対する条件
- 元素
- 電荷
- 結合手
- 水素の数
- 任意の SMARTS
「結合」に対する条件
- 結合次数
- 脂肪族 / 芳香族
- 環状 / 非環状
「リンカー」に対する条件
- 長さ
- 環構造を含む / 含まない
部分構造検索ツールはツールバーの ![]() をクリックするとご利用いただけます。
をクリックするとご利用いただけます。
Card View Version 2
従来よりも自由なデザインが可能になりました。縦横の寸法が自在に変化させられ、好きなテキストの追加ができます。また、ドラッグ&ドロップによって簡単にデータのレイアウトを変更できます。
新しい Card View のデモンストレーションは こちら をご覧ください。
さらに、新しいカードを既存のスタックに加える機能も追加されました。この機能により、クラスタリングのような解析を再度実行する必要がなくなるため、時間が節約され、Card View の配置も保つことができます。
その他の変更点
- 40以上の異なるエンドポイントをもつナレッジベースの毒性予測を提供する Derek Nexus モジュールが Lhasa Limited による最新のナレッジデータベースにアップデートされました。また、クライアントマシンのメモリへの負荷を減らすため、Derek Nexus の計算はサーバーマシン上で実行されるようになりました。
- Nova モジュールにおける構造変換ライブラリを拡張するための BIOSTER モジュールに、最新の論文から引用した約2,000の構造変換ルールが追加されました。
v6.2 で追加された機能
- SD ファイル読み込み時に原子座標を保持できるようになりました。従来は StarDrop 独自の内部的な表現が用いられていましたが、複数のプラットフォームを通して化合物のもつ固有の配向を保ちたいというお客様からのご要望にお応えしました。
- モデルサーバーを強化しました。スケーラビリティが改善され、サードパーティや内部モデルを通して多数の化合物が処理されます。
- 全ての StarDrop サーバーが 64bit に対応しました。
- ユーザーがスケッチして追加した分子の向きを制御できるようになりました。この機能を利用すると、ひとつの分子の向き制御すれば、データセット中の他分子の向きもそれに合わせて制御できます。
→関連情報:分子の向きを制御する方法
- いくつかの細かい機能の強化とバグを修正しました。例えば、共有ファイルを開いたときにファイルがロックされる機能の追加や、データ元に変更が合った際のプロジェクトファイルの更新やフローティングライセンスの管理におけるフレキシビリティの強化があります。
- StarDrop のスクリプティング API が原子座標にも対応しました。
v6.1 で追加された機能
Matched Series 解析
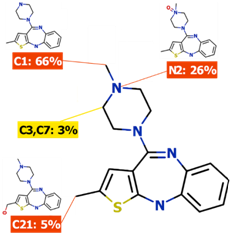
化合物の最適化のための新しい戦略を探索するStarDrop の Nova モジュールが、matched series 解析の追加により機能が強化されました。matched series 解析は NextMove Software 社と共同で開発し、置換基のみが異なる3つ以上の分子シリーズ (matched molecular series) を探索することで、ターゲットの活性を改善する置換基を特定します。置換基のみが異なる分子の数が多い分、一般的に用いられている置換基のみが異なる分子ペア (matched molecular pair) のアプローチよりも、追加の情報を与え、あなたの化学シリーズに適した提案を可能にします。
Nova には matched series 解析に基づく次の2つの方法が組み込まれています。ナレッジベースのデータベースで頻出のシリーズを用いて、あなたのデータの短いシリーズと一致させる Matsy™ (J. Med. Chem., 2014, 57(6), pp 2704–2713) と、分子のアクティビティについての測定値と強い相関をもち、より長いシリーズを用いるSAR transfer です。
matched series 解析はターゲットに対するアクティビティについての測定値をもち、置換基のみが異なる分子シリーズを1つ以上含むデータセットを入力します。解析を開始するためには、StarDrop のNova タブを選択し、ボタンをクリックして Nava セッションを起動し、Matched Series Suggestion を選びます。この機能についての簡単なデモンストレーションは こちら をご覧ください。
プロジェクトファイル形式
複数のデータセットや解析結果、グラフを含む StarDrop のセッションを全てまとめてひとつのプロジェクトファイルとして保存できるようになりました。これにより、すぐにデータセットを開いたり、共有することができます。StarDrop で最初にデータセットを開くと自動的にプロジェクトファイルが生成され、File メニューから保存すると、初期設定でプロジェクトファイル (.sdproj) として保存されます。もちろん、File メニューの Save Data As… から従来のようにデータセットごとの保存も可能です。
プロジェクトファイルの各データセットは、ファイルの読み込みやデータベースへの問合せなどの、データソースへの接続も可能です (データベースには StarDrop のスクリプティング API を通して適切に接続する必要があります) 。さらに、新しい化合物や結果が増えたときには、データを開き直さなくてもデータセットや計算、グラフを更新することができます。データソースからデータセットを更新するには、Data Set メニューから Refresh を選択します。
強化された P450 代謝モジュール
StarDrop の P450 モジュールはいくつかの点で強化されました。まず、既存の CYP3A4、CYP2D6、CYP2C9 アイソマーによる代謝予測モデルは、新しく質の高いデータセットを用いることで、改良されました。また、根底となる量子力学のモデルに、エポキシ化を含む反応経路を追加しました。さらに、CYP2C8、CYP2C19、CYP2E1、CYP1A2 アイソマーのモデルも追加されました。
その上、各部位が代謝された場合の代謝産物も予測されます。StarDrop の P450 タブで左下にある ![]() ボタンをクリックすると、代謝産物を確認することができ、別の解析のために新しいデータセットとして保存することもできます。
ボタンをクリックすると、代謝産物を確認することができ、別の解析のために新しいデータセットとして保存することもできます。
これらの新しい機能を使うためには、P450 モデルサーバーを更新する必要があります。
その他の強化された機能
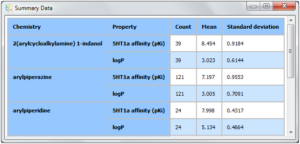
- Summary テーブル
この新しいツールは、データセットにおける物性値データを好きなカテゴリを軸に簡単にまとめてくれます。Summary テーブルを作成するためには、Tools メニューで Create Summary を選択します。テーブルは好きなカテゴリを軸に作成でき、プレゼン資料や報告書に編集可能なテーブルの形式でコピーペーストができます。また、プロジェクトファイル形式を使って保存、復元も可能です。簡単な紹介ムービーは こちら をご覧ください。
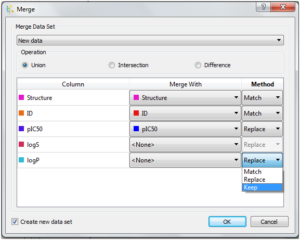
- 新しくなったファイル結合ツール (Merge ツール)
ファイル結合ツール (Merge ツール) の機能が拡張されました。Operation の設定が追加され、データセットを結合する Union と同じように、データセットの共通部分を探す Intersection、差異を見つける Differences が選択できます。どの列もデータセット間で一致させるために選択でき、もし2つのデータセットに異なる値があれば、元のデータセットの値をそのままにするのか、新しいデータセットの値を採用するのかの選択も列ごとに設定できます。
- R-group 解析におけるステレオケミストリー
StarDrop の R-Group 分解ツールがステレオケミストリーの処理について改良されました。新しい R-Group 解析は、R-Group を置換させた時点で局所的なステレオケミストリーの影響をうけ、E/Z 体で表される置換基を区別します。
v6.0 で追加された機能
Card View – 化合物データセットの新しい表示方法 –
Card View は、化合物とそれらの関係性を直感的にわかりやすく表す画期的で新しい化合物データセットの表示方法です。構造やさまざまな物性値を集約したカードは、自由に動かしたり、結びつけてグループを作成することができ、既存のスプレッドシートよりも最適な構造や重要な構造活性相関 (SAR) を見つけやすくします。Card View を利用することで、柔軟で対話的に化合物データを表示することが可能になります。

Card View の基本機能 1:Card
データセットは、化合物ごとに1枚のカードとして表示され、カードは自由に動かすことができます。カードに表示する情報は好きなようにカスタマイズすることができ、複数ページにわたってスペースを使用することができます。注目する物性値でカードの色付けをすることや気になるカードを横に並べて比較することで、これらの重要な違いを明らかにします。
Card View の基本機能 2:Stack
あるカードを別のカードの上に重ねる (Stack する) だけで簡単にグループを作成することができます。Stack すると一番上のカードには、ヒストグラムやボックスプロットを使って物性値の分布や、最大共通部分構造 (Maximum common substructure) を表示することができます。表示する物性値は、カードと同様にお好みに応じてカスタマイズすることができます。
Card View の基本機能 3:Link
カードは構造的な類似性や合成のステップのように関係性があるもの同士を結びつける (Link する) ことができます。Link には直線と矢印があり、直線は関連付けられる化合物同士を結びつけてネットワーク構造を構築することに利用でき、矢印でカード同士の関係に方向性を与えることにより、合成のステップや相対的な大小関係を表すことができます。さらに Link に色付けすれば、物性値が大きく変化する関係性やステップを明らかにします。
CardView を使用した解析機能
クラスタリングや Matched Molecular Pair (MMP) 解析、Activity Landscape (Activity Cliff) といった解析は、複雑なデータを解析する強力な手法ですが、これらの結果を解釈するためには、時間と労力を要する専門的な解析が必要なことが課題でした。しかし、この Card View を用いることで、これらの結果を直感的にだれもが解釈できるように表示することができます。
その他の機能強化
- データ解析機能の強化
- 共通部分構造によるクラスタリング (common substructure clustering)
- Matched Pair Analysis
- Activity Landscape
- Activity neighbourhood analysis (activity cliff の探索)
- Multi scaffold R-group 解析
- グラフ化機能の強化
- Derek Nexus モジュールの更新
